
上一期我们应用R和Epicale程序包对数据集outbreak定义完病例以后,分析了暴露的时间,本期让我们来看一下发作时间。这里应用R和Epicale程序包对这些数据进行分析。
首先,确认"onset"这个变量只用于病例。
onset[!case]<-NA
关于发作时间的计算方法与暴露时间的计算方法相同。
day.onset<-substr(onset,7,8) tab1(day.onset)
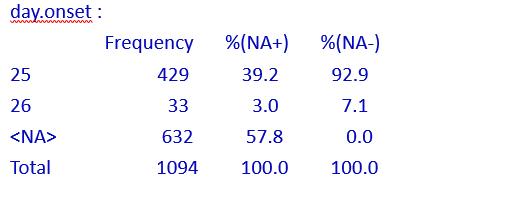
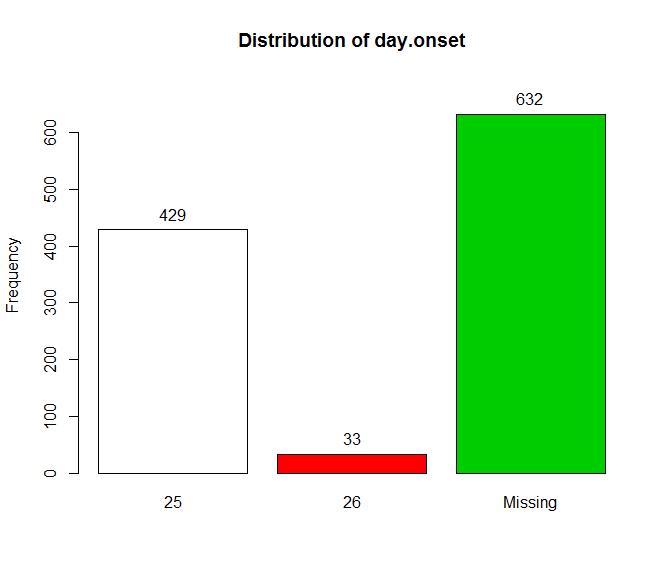
在所调查的对象中,对记录发作时间的变量day.onset,有57.8%的缺失值。这是由于被调查的对象没有症状,因而对象什么都记不起来。在报告了时间的对象中,92.9%发作于1990年8月25日,其余的7.1%是在这天之后发作的。
hr.onset<-substr(onset,9,10) tab1(hr.onset) min.onset<-substr(onset,11,12) tab1(min.onset) time.onset<-ISOdatetime(year=1990,month=8,day=day.onset,hour=hr.onset,min=min.onset,sec=0,tz="") label.var(time.onset,"time of onset")
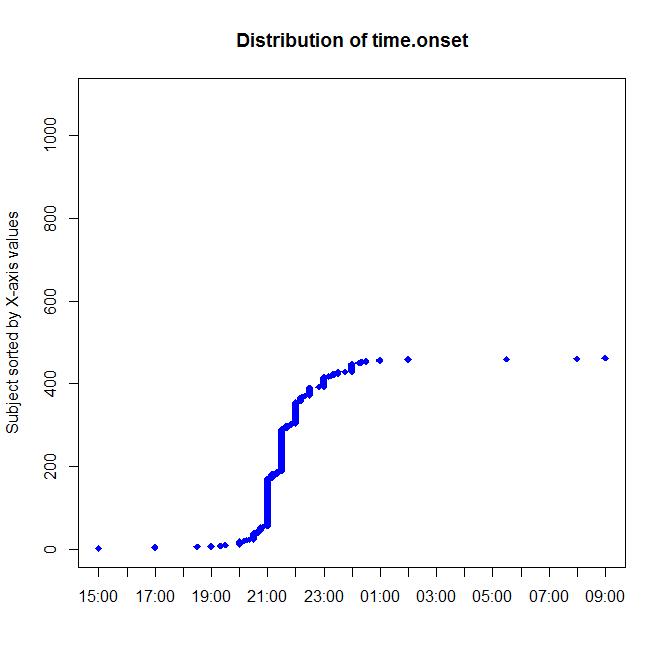
因为有很多缺失值,所以上图部分是空的。
散点图看起来会直观一些。
dotplot(time.onset)
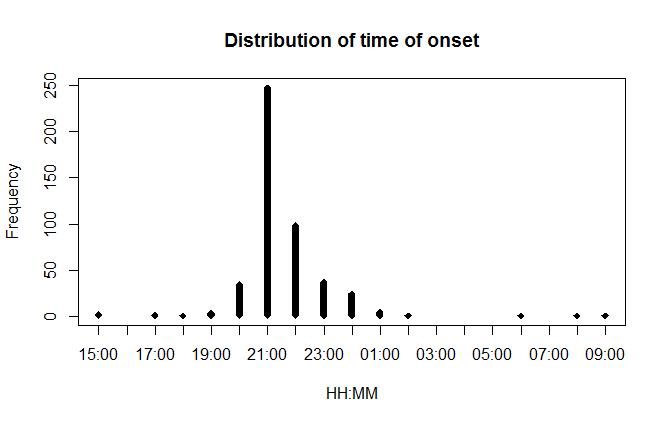
两个图都呈现了典型的单峰流行曲线,提示爆发的来源只有一个。最早的病例发作于8月5日下午3点,绝大多数病例发作于深夜。到第二天早上,就只有很少的病例了。最后报道的病例发作于8月26日上午9点。
潜伏期
对于潜伏期的分析就是很直接的了。
incubation.period<-time.onset-time.expose label.var(incubation.period,"incubation period") summ(incubation.period)

dotplot(incubation.period,las=1)
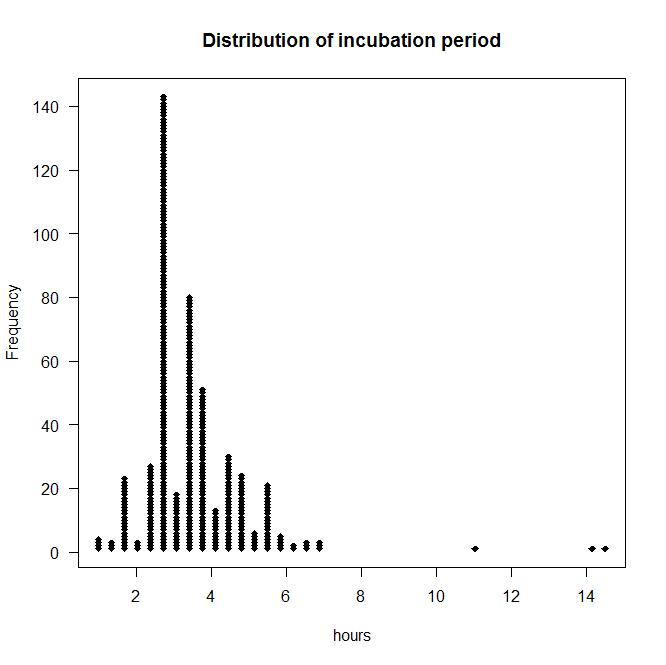
潜伏期呈现出右偏态,时间的中位数为3.5小数。