CNV拷贝数变异,听起来再熟悉不过了,关联分析的宣传最近也是铺天盖地,大家也都不陌生了。然而CNV的关联分析你造吗?今天小编为大家介绍一个科研界的“旧元素新组合”。
CNV对人类疾病的影响
CNV (copy number variation, CNV) 是人类主要的致病遗传因素之一,研究表明,多种疾病与CNV有关,如22q11.2的缺失是精神分类症的致病因素[1]、Santhosh等人发现1q21.2染色体区域CHD1L基因的重复是自闭症的风险因素[2]、DEFB4基因的多拷贝在克罗恩病患者中显著富集[3],以及8号染色体b防御素区基因拷贝数的增加是导致荷兰人银屑病的风险因素[4],CNV可通过影响基因剂量和染色体构象和基因活性对人类疾病产生影响。
CNV关联怎么做?
基于CNV的关联分析为科研工作者提供了不同的研究思路,通过对大样本人群的遗传数据进行分析,应用统计模型计算出患病人群(case)和正常对照组(control)间具有显著性差异的CNV,过滤一系列的低频有害等条件;除此之外,我们还会针对这些CNV进一步研究其影响的基因,以及在疾病相关功能通路中的富集情况,进行一下几个方面的分析:
1)全基因组范围内的CNV burden分析:比较case和control组的CNV数量,找出具有显著性差异的CNV;
2)基于通路的关联分析:选取与疾病相关的基因集进行关联,找出CNV在哪些通路中是显著性富集的;
3)基于基因的关联分析:将CNV定位到影响的基因,以基因为单位比较case和control组之间存在显著性差异的基因。

下面的这篇文章就是从这样的多层次来全面阐释CNV对疾病的影响的。
Contribution of copy number variants to schizophrenia from a genome-wide study of 41,321 subjects[1]
期刊:Nature Genetics 时间:2017年1月
影响因子:31.62
研究方法
共选择41,321个样本的芯片数据, 其中包含21,094 个精神分裂症病例和20,227个健康对照。保留两种软件检测结果一致的CNV, 保留罕见高质量的CNV(长度>20 kb, 至少覆盖10个探针, MAF<1%), 通过在4个水平上, 即全基因组范围、通路、基因、断点的水平上检测case和control具有显著性差异的CNV及受其影响的基因。
研究结果
1. 全基因组范围内的CNV burden分析
统计case和control组的全基因组范围的CNV,结果显示精神分裂症患者的CNV burden相比control组大大增加。
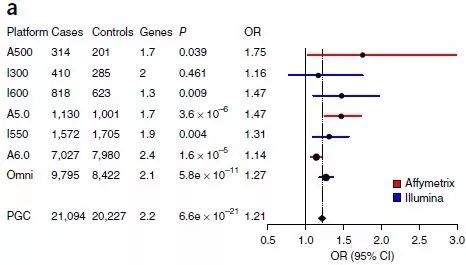
图1 全基因组范围内的CNV burden分析
2. 基于通路的关联分析
选择与精神疾病相关的包括神经功能、突触元件和神经发育等共36个通路(基因集),分别分析每个gene set 和CNV的类型(gain或loss)之间的关联。发现精神分裂症病例中富集了15个基因集的loss burden和4个gain burden。
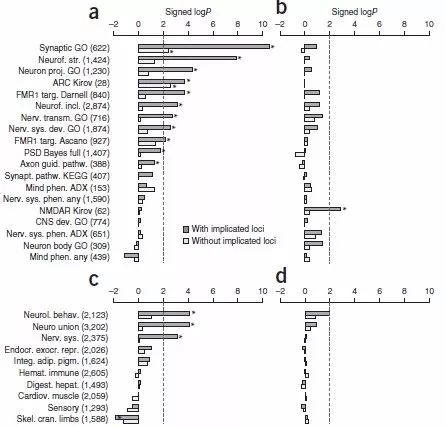
图2 通路关联的burden分析
“*”代表具有显著性的CNV富集通路
3. 基于基因的关联分析
为检测基因座位与疾病风险的关联,如果CNV覆盖到至少一个外显子则将CNV定位到该基因上,进而将这些基因进行关联分析。
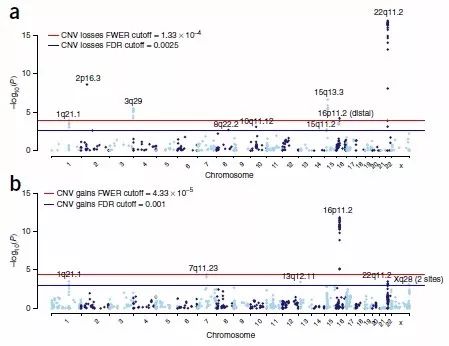
图3 基于基因关联的曼哈顿图
a 代表CNV缺失,b代表CNV增加。
4. 基于断点的关联分析
用SNP探针界定CNV的断点位置,对每个CNV断点进行关联分析。已有研究报道,位于染色体位置2p16.3的NRXN1基因就是一个CNV“hot spot”,该基因的外显子缺失在精神分裂症患者中显著富集。在本研究中,显著关联的断点主要位于转录起始位置和外显子上。
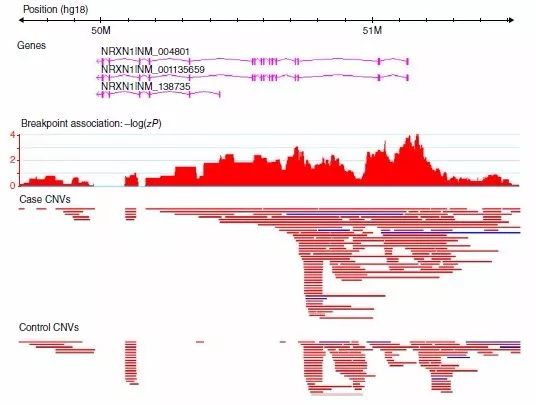
图4 NRXN1基因附近断点水平关联的曼哈顿图
红色代表缺失,蓝色代表增加。
除了这个案例,近来还有很多值得参考的文章,小编为您总结了一下:
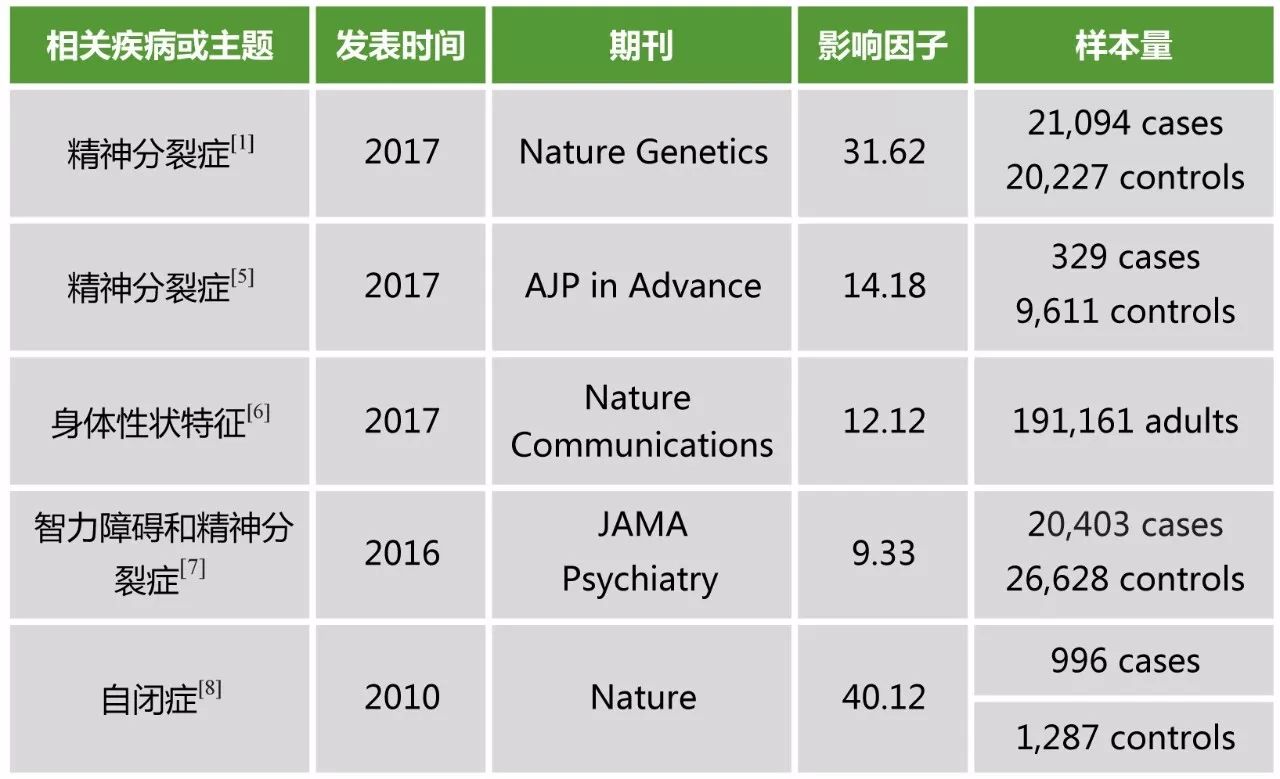
怎么样?如此深度剖析后,您了解CNV关联分析了吗?如果您感兴趣这样的分析,欢迎详询human@novogene.com。
参考文献
[1] Marshall CR, Howrigan DP, Merico D, et al. Contribution of copy number variants to schizophrenia from a genome-wide study of 41,321 subjects[J]. Nature Genetics, 2017; 49(10):1558.
[2] Girirajan S1, Dennis MY, Baker C, et al. Refinement and discovery of new hotspots of copy-number variation associated with autism spectrum disorder[J], The American Journal of Human Genetics, 2013, 92(2):221-37.
[3] Bentley RW, Pearson J, Gearry RB, et al. Association of higher DEFB4 genomic copy number with Crohn’s disease[J]. The American journal of gastroenterology, 2010; 105(2): 354-359.
[4] Hollox EJ, Huff meier U, Zeeuwen PL, et al. Psoriasis is associated with increased beta-defensin genomic copy number. Nat Genet 2008; 40: 23–25.
[5] Bassett A S, Lowther C, Merico D, et al. Rare Genome-Wide Copy Number Variation and Expression of Schizophrenia in 22q11. 2 Deletion Syndrome[J]. American Journal of Psychiatry, 2017; 174(11):1054-1063.
[6] Macé A, Tuke M A, Deelen P, et al. CNV-association meta-analysis in 191,161 European adults reveals new loci associated with anthropometric traits[J]. Nature Communications, 2017, 8(1): 744.
[7] Rees E, Kendall K, Pardiñas AF, et al. Analysis of Intellectual Disability Copy Number Variants for Association With Schizophrenia [J]. JAMA Psychiatry, 2016, 73(9):963-969.
[8] Pinto D, Pagnamenta AT, Klei L, et al. Functional impact of global rare copy number variation in autism spectrum disorders[J]. Nature, 2010, 466(7304):368-72.
疾病业务线 孟颖 | 文案