该篇实验方法已经在 eLife 文章“circFL-seq reveals full-length circular RNAs with rolling circular reverse transcription and nanopore sequencing”中验证过。原作者将该方法的详细版本发表在 Bio-protocol 期刊,欢迎大家进入 Bio-protocol 期刊直接与作者交流。
简 介
在这篇 Bio-protocol 文章中,来自北京大学医学部杨恩策团队开发了 一种高通量circRNA测序方法circFL-seq ,利用滚动循环逆转录(RCRT)和纳米孔长读长测序,从而在亚型水平更灵敏和精准的鉴定circRNA。

亮 点
1.本方法中的circFL-seq与short-read RNA-seq相比,滚动循环逆转录和纳米孔long-read测序使circRNA read丰富了10倍以上,在短(<100 nt)和长(> 2,000 nt)的circRNA转录本鉴定方面均显示出优势。
2.circFL-seq可以识别全长circRNA的差异选择性剪接,且与其他长读长测序方法相比,表现出更好的灵敏度和精度。使 circFL-seq成为大规模、高通量筛选功能性circRNA的潜在工具。
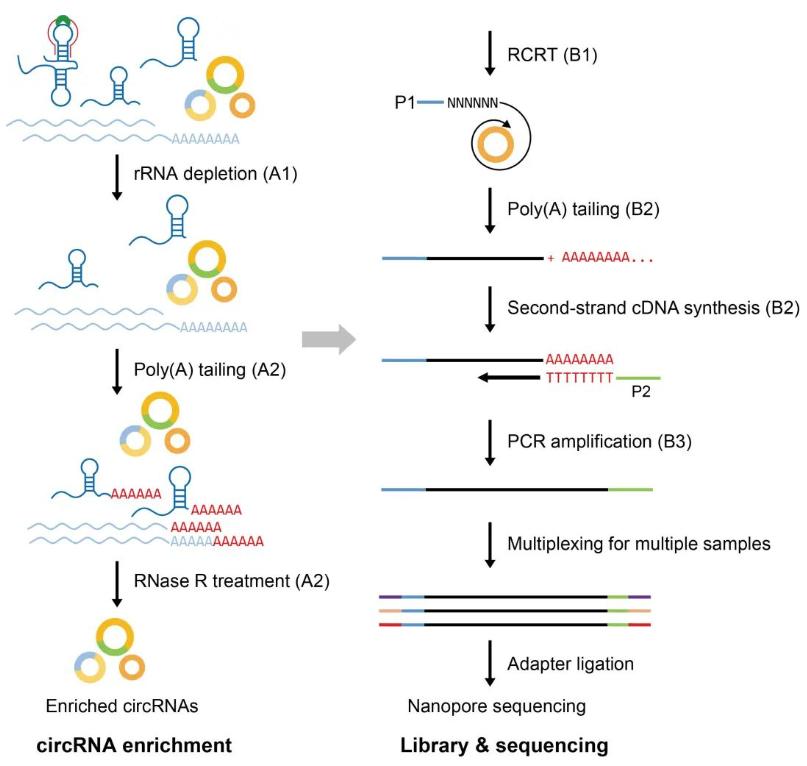
Figure 1. Experimental operation of circFL-seq consisted of circRNA enrichment, library construction, and nanopore sequencing.
背景介绍
环状RNA (circRNA)是一类通过反向剪接(BS)或套索前体形成的共价闭合RNA分子。传统的short-read RNA-seq方法通过使用深度测序检测circRNA的反向剪接点(BSJ)将circRNA与其线性同源物区分开来。适用于推断小于500 nt的circRNA的全长序列,但仅使用短读长是不可能全面了解circRNA亚型的。单分子长读长测序已显示出在亚型水平识别circRNA 的方法学进步。Pacific Biosciences (PacBio)测序已以低通量和高成本的方式应用于 PCR产品的目标全长circRNA序列。但是由于与线性同源的序列重叠,识别环状RNA (circRNA)的内部序列仍然是一个挑战。最近, 一种基于牛津纳米孔技术(ONT)的方法(如circFL-seq)已可用于全基因组全长 circRNA的重建。
步骤节选
step A. circRNA enrichment
A1. rRNA depletion
A2. Poly(A) tailing and RNase R treatment
step B. Full-length circRNA cDNA preparation
B1. Reverse transcription.
B2. Poly(A) tailing and second-strand synthesis
B3. Amplification
B4. Sample quality check
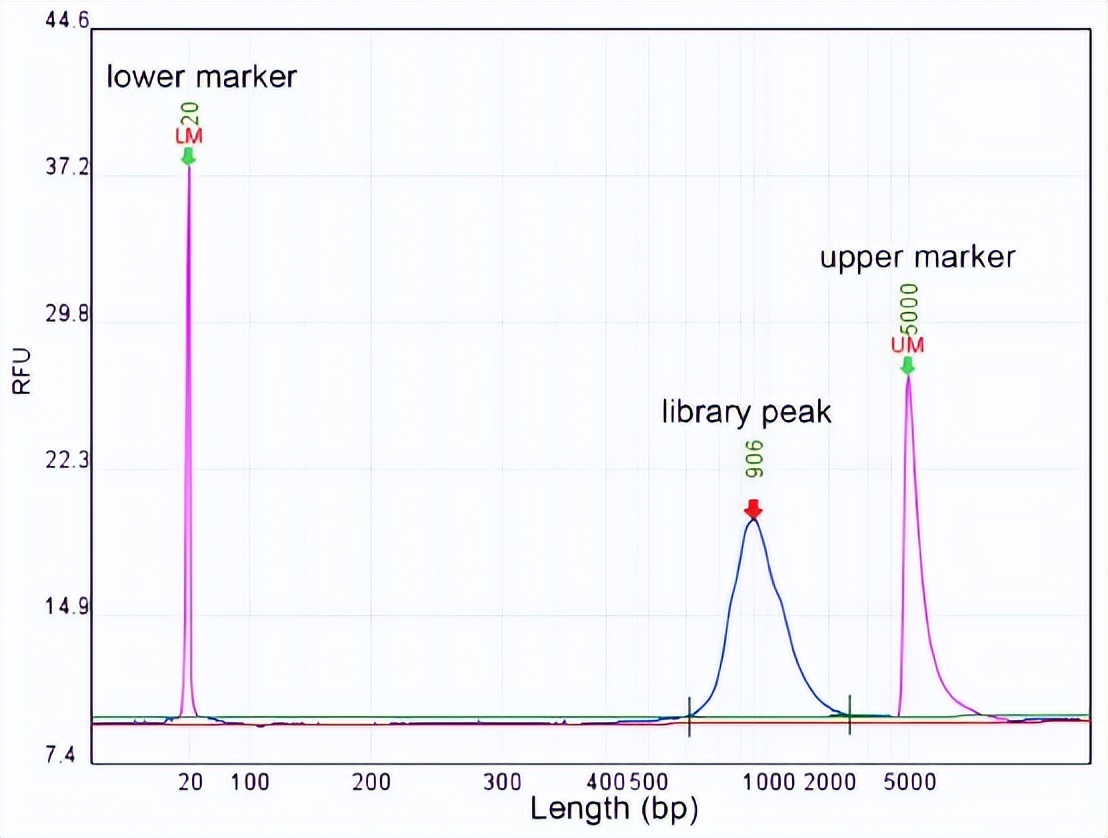
Figure 2. Length distribution of circFL-seq cDNA library.
step C. Nanopore library construction and sequencing
在 Bio-protocol 期刊查看原文,可以获取更多内容,包括摘要、背景、耗材试剂、仪器软件等详细信息。感兴趣的小伙伴,复制下方链接,一睹为快吧!
原文链接: https://s.bio-protocol.org?s=715466cbdbcfe7d1
END

Bio-protocol 简介
Bio-protocol于2011年在斯坦福大学创建, 致力于搭建全球权威的、高质量的生物实验方案分享平台,以助力科学发现。 Bio-protocol 期刊是Bio-protocol旗下的一份同行评审的国际学术期刊,发表高质量的生命科学实验方案,旨在提高科研的可重复性。至今, Bio-protocol 已发表了来自全球上万名优秀科研工作者(包括多名诺贝尔奖获得者)的4000多篇实验方案,并且同 Science 、 eLife 等12家国际权威科学杂志建立长期合作关系,共同促进生命科学研究的可重复性。2019年 Bio-protocol 期刊已被PubMed Central,ESCI收录。