文 | 玉惜品诗
编辑 | 玉惜品诗
«——【 ·引言· 】——»
沿海微生物垫是小规模且基本上封闭的生态系统,其中大量不同的微生物功能群负责元素的生物地球化学循环,本次研究中,通过16S rRNA基因标签测序分析方法,探究沿海微生物垫中古细菌的多样性。
实验中,对古细菌的功能基因进行分析,我们发现古细菌在沿海微生物垫中具有多样的功能特征,如硫代谢、甲烷代谢等,这些功能特征揭示了古细菌在沿海生态系统中的重要作用,为进一步研究古细菌的生态功能提供了基础。

«——【 ·16S rRNA 基因标签测序· 】——»
rRNA的高可变V6区域两侧的保守序列作为产生PCR扩增子的引物位点,为了捕获细菌16S rRNA基因序列的全部多样性,在V5区域的3'末端使用了6个引物。
对于古菌序列,使用一个5'引物和两个3'引物,每个PCR反应一式三份进行,将纯化的扩增子文库退火为寡核苷酸,寡核苷酸与拴在μm尺寸磁珠上的衔接子序列互补,退火条件设置为有利于每个磁珠一个片段。
对这些片段进行PCR扩增,每个磁珠产生约10万个相同拷贝的独特DNA模板,携带单链DNA克隆的珠子被沉积到孔中,以便在罗氏基因组测序仪上进行焦磷酸测序。

从原始数据的开始和结束修剪引物序列后,平均生成60 bps的序列读数,基于对焦磷酸测序错误率的评估,删除了低质量的序列,使用标签映射方法GAST(序列分类学的全局比对)进行比对和分类分配。
将序列读数与已知16S rRNA基因的参考数据库数据库获得进行比较,并根据RDP分类器进行分类分配。
通过显微镜鉴定,硅藻比其他站更丰富,ST3站位于ST1和ST2之间,其特点是微生物垫以不规则的间隔接收淡水和海水(主要是在春季潮汐时)。
ST3构成了盐沼生态系统的基础,部分生长着少数几种植物,显微镜检查显示,微紫薇是ST3中蓝藻的主要组,在较小程度上发现了河口乳杆菌,偶尔发现异囊和单细胞蓝藻。
ST1和ST3的微生物垫在最近沉积的细沙薄层下方含有绿色蓝藻层,而在ST2处观察到绿色/褐色层,在夏季和秋季,在ST1和ST3上注意到明显的紫色层,这在春季不存在,在ST2从未注意到,在所有站点上,在大约5-10毫米的深度都存在一个黑色的,富含硫化铁的地平线。
使用细菌V6引物,我们总共获得了169 338个序列,其中92%被鉴定为细菌,对于每个样品,我们平均获得了17 247个细菌序列读数,古菌V6引物的特异性较低。仔细检查,27 361个读数中只有85 415个(24%)是古菌,每个样本平均有3909个。
大多数读数似乎属于Eukarya。细菌单例的频率(样本中仅发生一次的唯一读数除以该样本中不同序列读数的总数)非常恒定,为0.69±0.01。古菌读数揭示了单例频率的类似守恒,尽管值更高,为0.79±0.03。

将相差不超过5%的标签聚类到操作分类单位(OTU)中,以计算稀疏和非参数估计量,细菌丰富度(样品中不同OTU的数量)和多样性(考虑OTU分布均匀性的香农H指数)在秋季发现最高,在春季最低,除了ST3在夏季具有最低值。
对于古菌部分,我们只有一个完整的ST2站数据集,该数据集显示出类似的趋势,秋季丰富度和多样性最高,春季最低,在ST3中,夏季古菌丰富度显著较高,而多样性估计量值最低。

在95%临界水平下对所有站点的细菌多样性进行稀有分析显示,曲线确实达到渐近线水平但尚未达到渐近线,而非参数统计分析表明观测到的丰富度覆盖了估计总细菌丰富度的60%至66%。
古菌丰富度的稀疏曲线也尚未达到渐近线,观测到的丰富度覆盖了估计古菌丰富度的74-80%,观察到的细菌丰富度比古菌丰富度高6至29倍,香农和辛普森多样性指数也表明,相对于古菌种群,细菌种群的多样性更高。

细菌群落的空间与时间多样性模式门水平的聚类分析揭示了特定垫子类型中群落组成的及时保存。台站ST3和ST1更相似,并且与台站ST2分开聚集,秋季和春季群落组成彼此之间比ST2和ST3的夏季群落更相似,而ST1的春季和夏季群落组成彼此之间更相似,而不是秋季群落。
在目级比较分类组成时也获得了类似的结果,在古菌群落中也发现了类似的分布;台站ST1和ST3聚集在一起,它们的组成与ST2不同。
«——【 ·古菌群落的稳定· 】——»
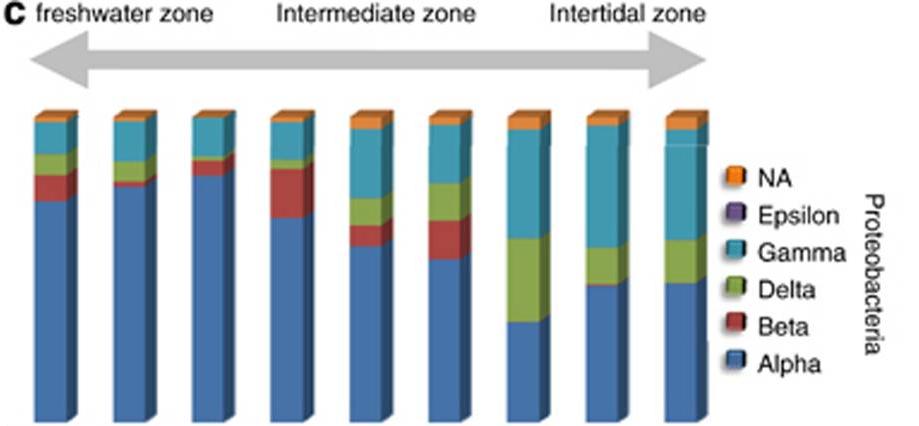
获得的分类学数据涵盖了广泛的已知细菌门,候选门OP8,BRC1,OP11,OP3,OP10,TG1和JS1仅由少数序列表示(<25,。所有样品中的优势门属于变形杆菌、细菌、蓝藻和放线菌。
揭示了站点 ST1/ST3 和 ST2 之间的巨大差异,后者的特征是前 10 名中没有蓝藻序列,ST3和ST2中丰富的黄杆菌科没有出现在ST10的前1名中,除优势门外,在所有三种垫子类型中都发现了大量与疣状微生物、厚壁菌、扁平菌纲、绿弹性菌、酸杆菌相关的序列读数。
一小部分(1.4-3.3%)的读数不能被分配到域水平以下,并被指定为细菌NA,在变形杆菌中,α变形杆菌占ST1(>70%的变形杆菌)和ST3(>50%的变形杆菌).α变形杆菌主要由属于红杆菌目和鞘磷脂单胞菌目。
在ST2站,α-(主要是红杆菌)、δ-(主要是脱硫杆菌和粘球菌)分布更均匀,一种潜在的新型伽马细菌不能被分配到类水平以下,在β变形杆菌中,伯克霍尔代菌在ST1和ST3中占主导地位,但在ST2中几乎不存在。

细菌以黄杆菌和鞘杆菌为代表,与黄杆菌相关的序列在ST2*特中**别高,在秋季种群中达到高峰,在夏季最小,在ST1和ST3中也观察到了类似的趋势,鞘杆菌在所有三个站点的秋季种群中达到顶峰。
蓝藻序列在ST1和ST3中大量存在,并且由我们无法在门水平以下分配的成员主导(71-96%),属于蓝藻组GpIV,GpI,GXIII的序列在ST1和ST3中也有很好的代表性,ST2站仅显示少数蓝藻序列。

放线菌中,放线菌目和NA放线菌目在所有站点均占主导地位,较少的读数被分配给酸性微生物和红杆菌目,放线菌以ST2中读完次数最多的NA家族为代表,特别是在秋季和夏季,微细菌科放线菌家族在ST1和ST3*特中**别丰富,在ST2中几乎不存在。
ST3的春季群落包含盐杆菌,ST2站与其他两个站的不同之处在于有更多的NA古菌,ST2的春季和夏季群落以甲烷微生物为主,而秋季群落则揭示了更多的热蛋白,在ST2中,卤杆菌仅以少量存在。
ST2的古菌群落组成趋于稳定,而ST1和ST3的组成则波动较大,在ST1中,甲烷菌在秋季主导了社区,并在次年夏天被甲烷微生物所取代,连续几年的长期分析应表明这是否是产甲烷群落响应垫成熟而发生的年度变化的一部分,或者这是否是一次性事件。
对于生态系统功能,这种变化可能影响不大,因为两者都参与甲烷生成,在ST3中,古菌部分以盐杆菌为主,,在夏季,观察到的丰富度为96%归因于嗜盐古菌,这些夏季样本是在几周的高温和低降雨量导致干燥和局部盐度增加后采集的,为嗜盐生物让路。

典型细菌嗜盐杆菌属的序列在ST3的夏季群落中略有增加,而耐盐卤色素的序列主要存在于ST1的夏季群落中,在夏季社区中并未显示更高的数量。
尽管夏季条件更恶劣,有利于嗜盐菌的生长,但ST3的多样性(H=5.8)仅略低于秋季和春季(H=6.1),非盐耐受微生物被大量的细胞外聚合物物质保护免受干燥。

«——【 ·结论· 】——»
微生物垫在沙滩上的定氮作用促进了植被在沙滩上的生长,微生物垫中的光合细菌通过发酵和光呼吸过程排出的低分子有机化合物作为底物,为硫酸盐还原菌(SRB)提供了生长的条件。
微生物垫中的放线菌也丰富多样,具有分解复杂有机物的能力,对碳的降解具有重要作用,通过16S rRNA基因标签测序分析揭示了沿海微生物垫中古细菌的多样性,并初步探索了其地理和季节分布特征以及功能特征,对于深入理解沿海生态系统的结构和功能,以及古细菌在其中的生态角色具有重要意义。
参考文献:
多伊卡马,斯塔尔,《嗜热产甲烷细菌的二氮固定》
贝布特,博世克,《蓝藻门含氧光合细菌》
伯恩斯,施普林格,《海洋微生物垫中二甲基硫醚的动力学》